密点麻蜥(
Eremias multiocellata)属有鳞目(Reptilia)蜥蜴亚目(Squamata)蜥蜴科(Lacertidae)麻蜥属(
Eremias),是卵胎生变温动物,主要以昆虫为食
[1],常见于北部和西北部的荒漠草原和半荒漠草原
[2]。该物种不仅在维持生态平衡方面具有重要作用,还是一种具有较大开发潜力的动物药
[3]。目前,有关其药用作用的研究越来越多,如应用密点麻蜥治疗肝炎肝纤维化已取得较好疗效,其可有效改善患者症状
[4];其具有较好的抑制人胃癌MKN45细胞铁死亡的作用
[5],因此加强对野生密点麻蜥种质资源的保护和开发利用具有重要的现实意义。
线粒体DNA作为重要的遗传信息载体之一,具有相对分子量低、结构简单、拷贝数高、母系遗传和无重组等特点,常用于物种鉴定、母系数量、系统发育和起源分析等
[6]。线粒体
ATP6基因在细胞能量代谢、遗传稳定性、疾病相关性、编辑位点多样性和单拷贝性等方面发挥着重要作用,使细胞能够高效产生能量、准确传递遗传信息、适应不同环境和生理条件,以及维持细胞功能的正常进行。另外,
ATP6编码的ATP合酶a亚基对蛋白质结构与作用的研究具有重要价值。线粒体控制区(D-loop)位于
tRNAPro 和
rRNAPhe 基因之间,不参与编码蛋白,是mtDNA序列中变异较大的区域,进化速度快,适用于亲缘关系较近群体间的比较和种群水平的差异研究
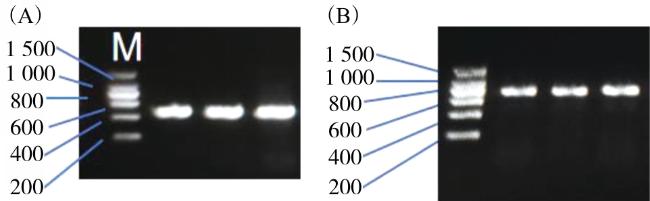
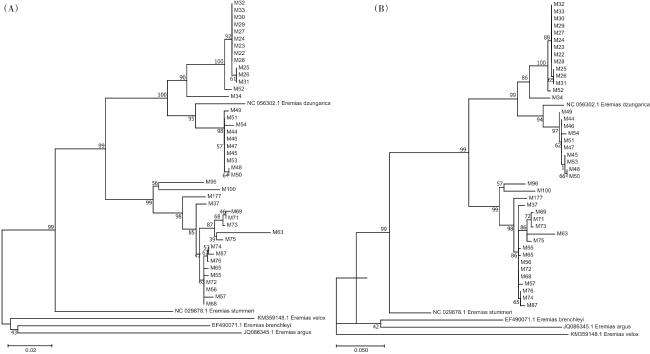
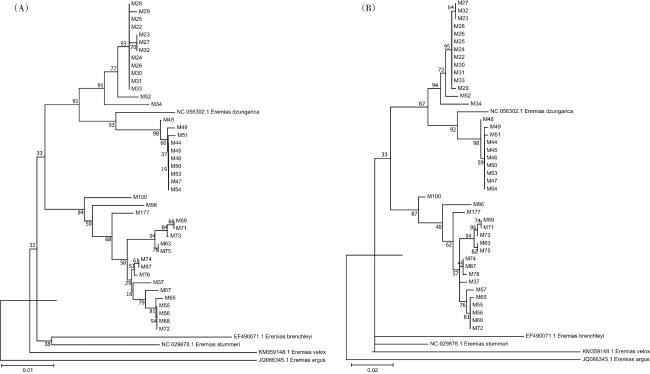
[7]。本研究以甘肃、宁夏和内蒙古地区的8个采样区域共计42只密点麻蜥为研究对象,对其线粒体
ATP6基因和D-loop区序列进行扩增,然后进行遗传多样性和系统发育分析,以补充西北部分地区的密点麻蜥基础遗传资源,为保护和开发其种质资源提供参考。